NGS ist die neueste Technik der molekulargenetischen Untersuchung, die es ermöglicht, effizient eine große Menge genetischer Sequenzen (DNA-Abschnitte) gleichzeitig zu „lesen“. Es ist eine Methode mit großem Potenzial für weitere Entwicklung und breite Anwendung bei allen Arten von genetischen Untersuchungen (gezielte Sequenzen/Gene und das gesamte Genom), einschließlich der Möglichkeit, sie in einem Experiment zu kombinieren. Die Methode NGS (mit sogenannter niedriger Abdeckung) kann auch für das präimplantationsgenetische Screening numerischer Chromosomenveränderungen (PGS (PGT-A)) oder für das präimplantationsgenetische Testen unbalancierter Formen familiärer Chromosomenumstrukturierungen (PGT-SR) in Verbindung mit dem Screening numerischer Veränderungen anderer Chromosomen verwendet werden.
Wenn die Analyse an einer Probe des Trophoektoderms durchgeführt wird, ist es dank der höheren Sensitivität der Quantifizierung, des verbesserten dynamischen Bereichs der Veränderungen und der besseren Unterscheidung des Signals vom Hintergrund möglich, das Vorhandensein mosaikartiger Veränderungen zuverlässiger zu beurteilen (als bei früher durchgeführten Untersuchungen mit Array-komparativer genomischer Hybridisierung (aCGH)). Ein Befund einer Chromosomenaberration in Mosaik bedeutet, dass in der Probe bzw. im Embryo, aus dem die Probe entnommen wurde, eine normale (euploide) Zelllinie und gleichzeitig eine aneuploide Linie vorhanden ist. Diese Veränderungen sind immer mit de novo entstandenen Chromosomenaberrationen verbunden, die im Rahmen der Untersuchung PGS (PGT-A) nachgewiesen werden. In einer Situation, in der kein (verbleibendes) Embryo mit normalem Befund vorhanden ist, kann nach entsprechender genetischer Beratung und nach Unterzeichnung einer informierten Einwilligung der Transfer eines Embryos mit mosaikartiger Aberration in Betracht gezogen werden.
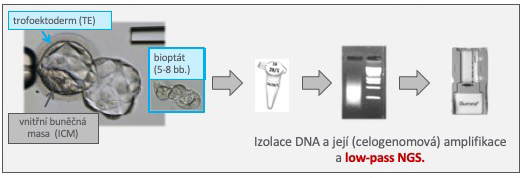
Prinzip der NGS-Methode: Aus den entnommenen Zellen wird DNA extrahiert, bei der anschließend eine gesamtheitliche Genomamplifikation (whole genome amplification, WGA) durchgeführt wird. Aus erfolgreich amplifizierten Proben werden enzymatisch sogenannte „Bibliotheken“ erstellt, die für das gleichzeitige „Lesen“ vieler DNA-Sequenzen geeignet sind. Jede Probe/Bibliothek hat eine einzigartige Kennzeichnung, die es erlaubt, in einem Experiment die DNA mehrerer Individuen (Embryonen) gleichzeitig zu analysieren. Die Proben/Bibliotheken werden im gleichen Verhältnis gemischt und die resultierende Bibliothek wird anschließend für das abschließende Sequenzieren vorbereitet. Das eigentliche Lesen der Sequenz (Sequenzierung) erfolgt durch die schrittweise Synthese neuer komplementärer DNA-Stränge zu den gelesenen Fragmenten. Die gelesenen Sequenzen werden mit spezieller Software mit dem normalen menschlichen Genom verglichen, ihre genomische Position wird bestimmt. Nach der Zuordnung der Sequenzen zu den einzelnen Proben wird eine quantitative Bewertung aller Chromosomen durchgeführt.
Einschränkungen der NGS-Methode: Die verwendete NGS-Methode mit niedriger Abdeckung (low-pass whole genome sequencing) ist durch die Größe der Chromosomenumstrukturierungen begrenzt. Kleine Verluste oder Gewinne von Chromosomen können nicht aufgedeckt werden und es können gleichzeitig keine weiteren Krankheiten oder Entwicklungsstörungen des Fötus ausgeschlossen werden, die nicht durch eine Veränderung der Anzahl der untersuchten Chromosomen oder ihrer größeren Teile verursacht werden.
Schema der NGS-Untersuchung – PGT-A, PGT-SR